ベイジアンネットワーク(CBNplot)で読み解く特発性肺線維症(IPF)— 後編:ネットワークから因果のストーリーを引き出す
はじめに
前編では CBNplot の bnpathplot() と bngeneplot() を使って、IPF のパスウェイネットワークを描きました。
ネットワークが描けると、次の疑問が生まれます。
「このネットワークから、何が起きてどうなったのかを、客観的に言うにはどうすればよいか?」
後編ではこの問いに答えます。ネットワーク理論の指標でパスウェイの「役割」を定義し、因果の流れを可視化し、ハブ遺伝子を既知の疾患データベースで検証する——という3ステップで、データから客観的なナラティブを引き出します。
Step 5:ネットワーク内の役割を定義する
描かれたネットワークのすべてのノード(パスウェイ)を、igraph を使って定量的に評価しました。
4つの役割
| 役割 | 定義 | 生物学的な意味 |
|---|---|---|
| Source (Driver) | in-degree = 0(受け取る矢印がない) | ネットワークの起点。他を駆動するが、自分は上流を持たない |
| Hub (Bridge) | 媒介中心性 > 中央値かつ双方向 | 上流と下流をつなぐ中継点。情報フローのボトルネック |
| Intermediate | 双方向だが中心性が低い | 中間的な経路 |
| Sink (Outcome) | out-degree = 0(出る矢印がない) | 最終的なアウトカム。上流から影響を受けるのみ |
「媒介中心性(betweenness centrality)」は、あるノードが他のノード間の最短経路上にどれだけ頻繁に登場するかを表す指標です。値が高いほど、ネットワーク内で「橋渡し役」として機能していることを意味します。
GO:BP の中心性分析
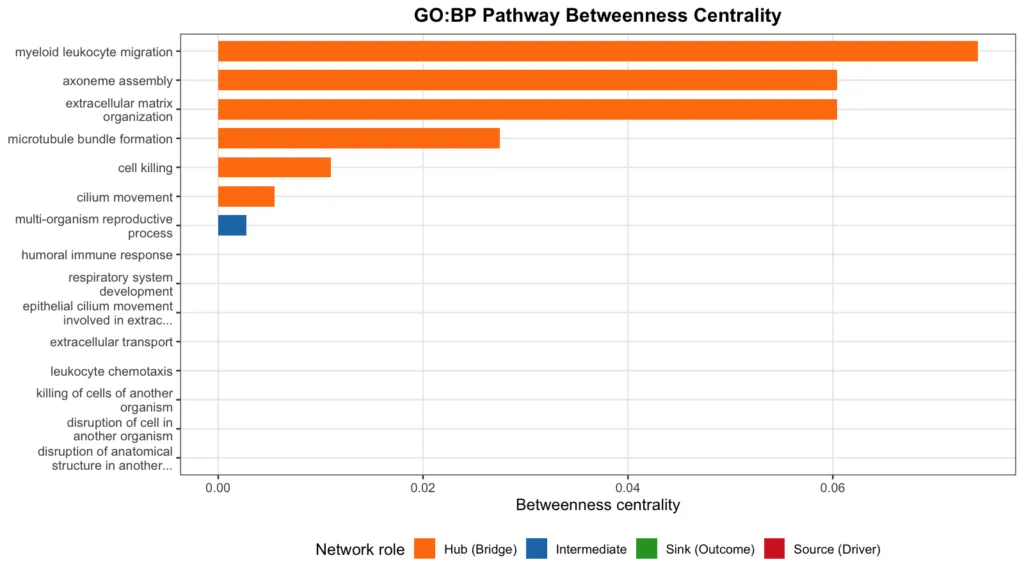
Reactome の中心性分析
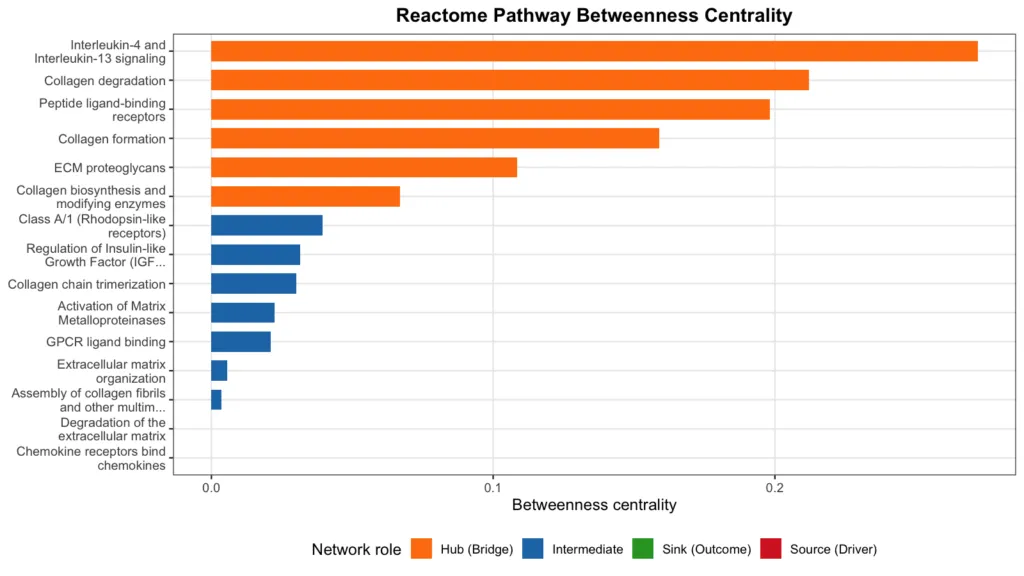
Reactome では、Extracellular matrix organization と Collagen degradation が特に高い媒介中心性を示しており、ECM 分解と線維化の接続点として機能していることがわかります。
Step 6:因果の流れを可視化する
役割の分類ができたら、次は「左から右へ因果が流れる」図として可視化します。Sugiyama レイアウトという階層的グラフ配置を使い、Driver を左端・Outcome を右端に固定して描きます。
-
ノードの色 = 役割(赤 = Driver、橙 = Hub、青 = Intermediate、緑 = Outcome)
-
ノードの大きさ = 媒介中心性(重要なパスウェイほど大きい)
-
矢印の太さ = Bayesian edge strength
GO:BP 因果フロー
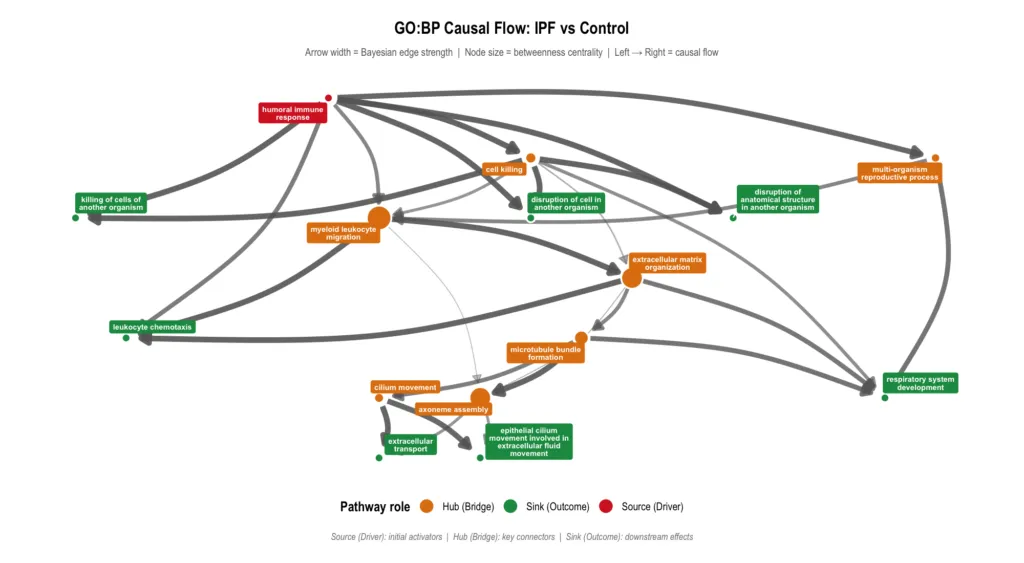
Humoral immune response(赤=Driver)が左端に位置し、Extracellular matrix organization と Myeloid leukocyte migration(橙=Hub)を経由して、Leukocyte chemotaxis や Respiratory system development の障害(緑=Outcome)へと流れる因果の構造が一目で読み取れます。
Reactome 因果フロー
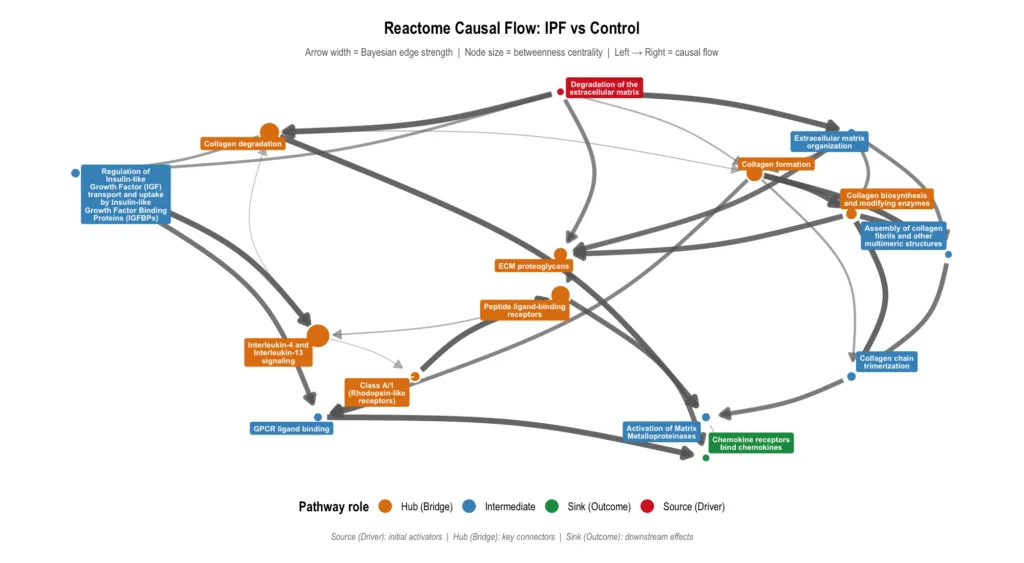
Reactome では Degradation of the extracellular matrix(赤=Driver)が起点となり、コラーゲン合成・分解・ECM 構築という一連のハブを通って、最終的に Chemokine receptors bind chemokines(緑=Outcome)に収束します。
ECM の「壊す・作る・組み直す」という一連のプロセスが、最終的にケモカインシグナルによる慢性炎症を引き起こす——という線維化の病態がネットワークとして見えてきます。
Step 7:ハブ遺伝子を疾患データベースで検証する
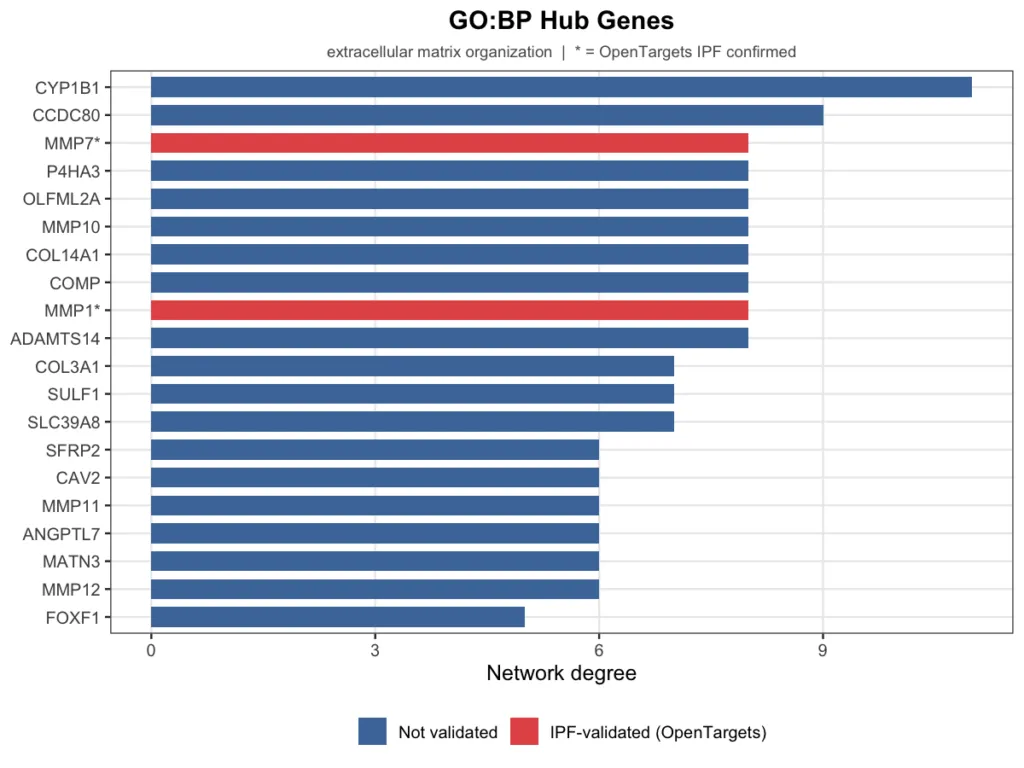
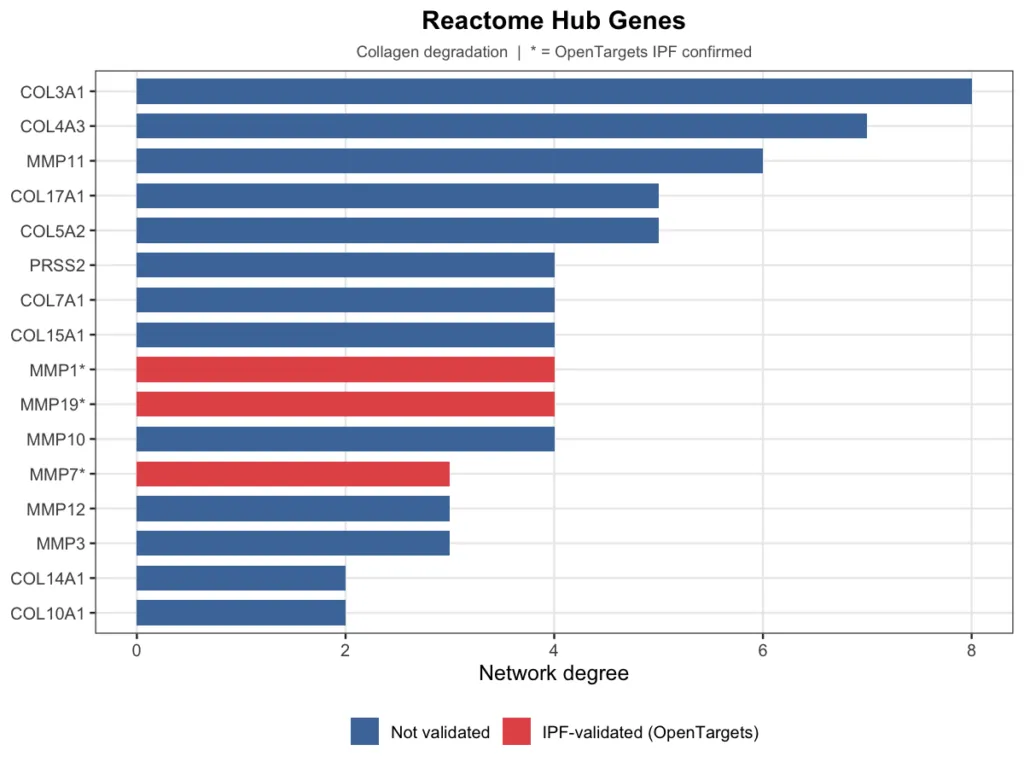
パスウェイネットワークのハブ(媒介中心性が高いパスウェイ)の内部で、どの遺伝子が中心的に動いているかを特定しました。GO:BP のハブは Extracellular matrix organization、Reactome のハブは Collagen degradation です。それぞれのパスウェイ内で bngeneplot() によって得られた遺伝子間ネットワークの degree 上位遺伝子を可視化し、IPF の既知治療標的データベース OpenTargets(疾患 ID:EFO_0000768)と照合しました。
図中の棒グラフの赤色(遺伝子名末尾に *)は OpenTargets で IPF 関連が確認されている遺伝子、青色は未確認の遺伝子を示します。
GO:BP のハブ遺伝子(Extracellular matrix organization)
Reactome のハブ遺伝子(Collagen degradation)
注目される遺伝子:
| 遺伝子 | log2FC | OpenTargets IPF 関連 | 備考 |
|---|---|---|---|
| MMP1 | +4.7 | ✓ 確認済み | コラーゲン分解の中核 MMP。ECM 分解ハブの上位遺伝子 |
| MMP7 | +3.0 | ✓ 確認済み | IPF の血清バイオマーカーとして臨床研究で広く使用 |
| COMP | +3.1 | — | 軟骨オリゴマーマトリクスタンパク。ECM の構造維持に関与 |
| MMP10 | +2.8 | — | ストロメライシン-2。MMP1 と協調して ECM を分解 |
| COL17A1 | +4.1 | — | 基底膜構成コラーゲン。上皮-間葉転換のマーカー |
| MMP11 | +2.3 | — | ストロメライシン-3。コラーゲン分解パスウェイ内で高 degree |
| COL3A1 | +2.1 | — | III 型コラーゲン。線維化組織での主要コラーゲン |
OpenTargets で確認されている MMP1・MMP7 はいずれも両ハブパスウェイで degree 上位に登場しており、既知の疾患関連遺伝子がネットワークの因果構造においても中心的な役割を担っていることが客観的に示されました。
データから自動生成される客観的ナラティブ
本解析では、ネットワーク構造・DEG の logFC・OpenTargets スコアの3つを組み合わせて、以下のようなナラティブをデータから自動的に導出するスクリプトも実装しました。
Reactome から導出されたナラティブ
【Driver】Degradation of the extracellular matrix が活性化(主に発現上昇)
— キー遺伝子:MMP1(+4.7*)、COL17A1(+4.1)、SPP1(+3.2*)、MMP7(+3.0*)
— うち 3遺伝子が OpenTargets で IPF 関連を確認済み↓ Bayesian strength 0.52
【Hub】Collagen degradation
— MMP1(+4.7*)、COL17A1(+4.1)、MMP7(+3.0*)、MMP10(+2.8) — 2遺伝子 OpenTargets 確認済み↓
【Hub】Collagen formation / Collagen biosynthesis and modifying enzymes
— COL17A1(+4.1)、ADAMTS14(+2.4)、COL3A1(+2.1) が有意に上昇↓
【Intermediate】Activation of Matrix Metalloproteinases
— MMP1(+4.7*)、MMP7(+3.0*)、MMP10(+2.8)、MMP11(+2.3) が一斉上昇 — 2遺伝子 OpenTargets 確認済み↓ Bayesian strength 0.82
【Intermediate】Extracellular matrix organization
— MMP1(+4.7*)、COL17A1(+4.1)、SPP1(+3.2*)、COMP(+3.1)↓
【Outcome】Chemokine receptors bind chemokines
— CXCL13(+2.8)、CCL7(+2.4)、CXCL6(+2.1) が上昇
この記述はすべて数値から自動的に生成されており、主観的な解釈を含みません。「IPF では MMP1・SPP1・MMP7 主導の ECM 分解が起点となり、コラーゲン代謝のハブを通じて、CXCL13・CCL7 によるケモカイン駆動の慢性炎症に収束する」という仮説は、データが客観的に語っている内容です。
GO:BP から導出されたナラティブ
【Driver】Humoral immune response が活性化
— MMP7(+3.0*)、CXCL13(+2.8)、CCL7(+2.4) — 1遺伝子 OpenTargets 確認済み↓ Bayesian strength 1.00
【Hub】Myeloid leukocyte migration
— CXCL13(+2.8)、GREM1(+2.7)、CCL7(+2.4) が上昇↓ Bayesian strength 1.00
【Hub】Extracellular matrix organization
— MMP1(+4.7*)、COMP(+3.1)、MMP7(+3.0*)、MMP10(+2.8) — 2遺伝子 OpenTargets 確認済み↓ Bayesian strength 0.82
【Outcome】Leukocyte chemotaxis / Respiratory system development の障害
GO:BP と Reactome で独立に得られたナラティブが、「ECM 再構成 → ケモカイン駆動の炎症」という共通のストーリーに収束していることは、この解釈の妥当性を支持します。
全体のまとめ
2記事にわたって、CBNplot を使った IPF の分子ネットワーク解析を解説しました。
| 解析 | ツール | 得られたもの |
|---|---|---|
| DEG 同定 | limma | 線維化・炎症遺伝子の変動リスト |
| パスウェイ濃縮 | GO:BP + Reactome | ECM・コラーゲン・免疫応答の有意な変動 |
| bnpathplot | CBNplot | パスウェイ間の因果方向と依存強度 |
| bngeneplot | CBNplot | パスウェイ内の遺伝子間ネットワーク |
| 役割分類 | igraph | Driver / Hub / Outcome の客観的定義 |
| 因果フロー図 | ggraph(Sugiyama) | 左→右の因果方向の可視化 |
| ハブ遺伝子検証 | OpenTargets API | 疾患関連性の客観的担保 |
CBNplot が提供する本質的な価値は、「パスウェイのリスト」を「因果のストーリー」に変換することです。