はじめに
「どのパスウェイが有意だった」——遺伝子発現データを解析すると、よくこういう結論になります。でもそれだけでは、何が何を引き起こしているのかはわかりません。
CBNplot はそこを一歩先へ進めるための R パッケージです。ベイジアンネットワーク(Bayesian Network)という統計手法を使って、パスウェイ間・遺伝子間の「依存関係」と「方向性」を学習し、因果の流れとして可視化します。
本記事(前編)では、公開データを使って CBNplot の基本的な使い方を実践します。対象疾患は特発性肺線維症(IPF)——原因不明の進行性肺線維症で、有効な治療法が限られる難治性疾患です。
**後編**では、このネットワークからさらに踏み込んで「何が起きてどうなったか」という因果のストーリーを客観的に抽出する方法を解説します。
使用データ
GSE47460(NCBI GEO)— IPF 患者と健常者の肺組織マイクロアレイデータです。今回は GPL14550 プラットフォームの 220サンプル(IPF 患者+健常コントロール)を使用しました。
サンプル数が多いほどベイジアンネットワークの学習精度が上がります。CBNplot を試すなら、できるだけサンプル数の多いデータセットを選ぶのがポイントです。
使用パッケージ:
-
limma— マイクロアレイの発現変動解析 -
clusterProfiler— GO:BP パスウェイ濃縮解析 -
ReactomePA— Reactome パスウェイ濃縮解析 -
CBNplot— ベイジアンネットワークの構築と可視化
Step 1:発現変動遺伝子(DEG)の同定
まず limma を使い、IPF vs コントロールで有意に発現が変動している遺伝子を同定しました(adj.P < 0.05、|log2FC| > 1)。
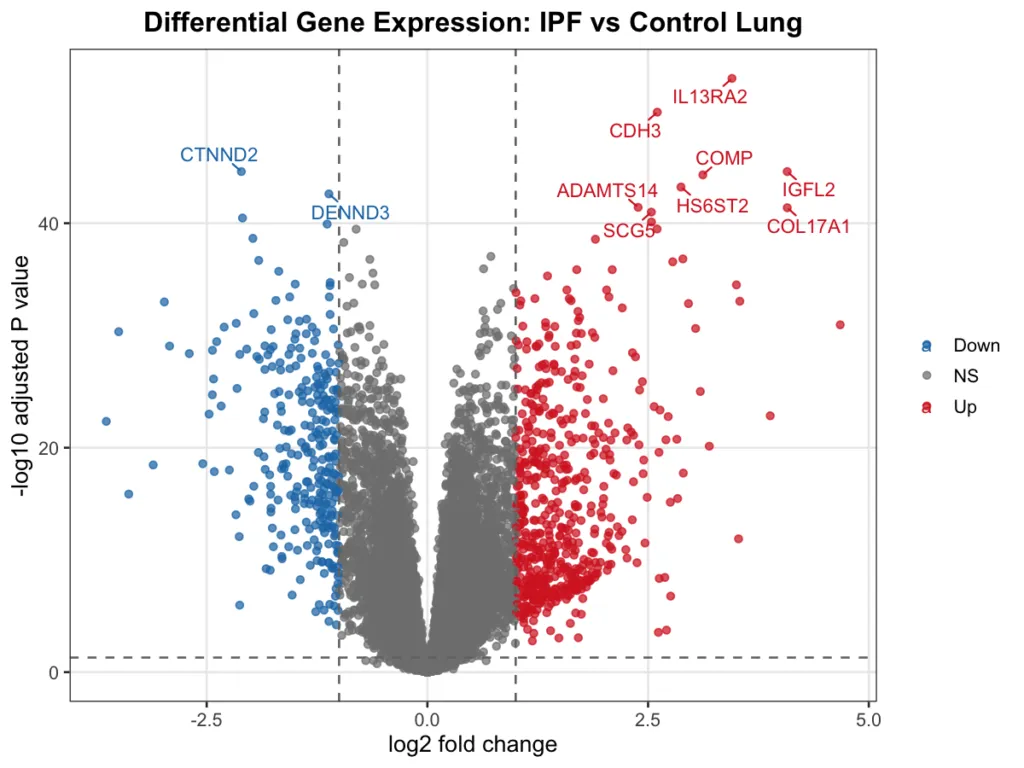
ボルケーノプロットの赤い点が「上昇した遺伝子」、青い点が「低下した遺伝子」です。上位に来た遺伝子を見ると、IPF の病態がすでに透けて見えます。
| 遺伝子 | log2FC | 役割 |
|---|---|---|
| MMP1 | +4.7 | コラーゲン分解酵素(ECM 分解の中核) |
| COL17A1 | +4.1 | コラーゲン XVII型(基底膜構成成分) |
| SPP1 | +3.2 | 骨橋タンパク(線維化促進因子) |
| CXCL13 | +2.8 | B 細胞誘引ケモカイン(慢性炎症) |
| MMP7 | +3.0 | IPF の血清バイオマーカー(臨床研究で広く使用) |
コラーゲン・MMPs(マトリクスメタロプロテアーゼ)・ケモカインが上位を占めており、線維化と慢性炎症が同時に進行しているIPFの病態を反映しています。
Step 2:パスウェイ濃縮解析
変動遺伝子群がどのような生物学的プロセスに集中しているかを調べました。GO:BP と Reactome の 2つのデータベースを並行して解析することで、広い視野(GO:BP)と機構的な詳細(Reactome)の両方を把握できます。
GO:BP(Gene Ontology 生物学的プロセス)
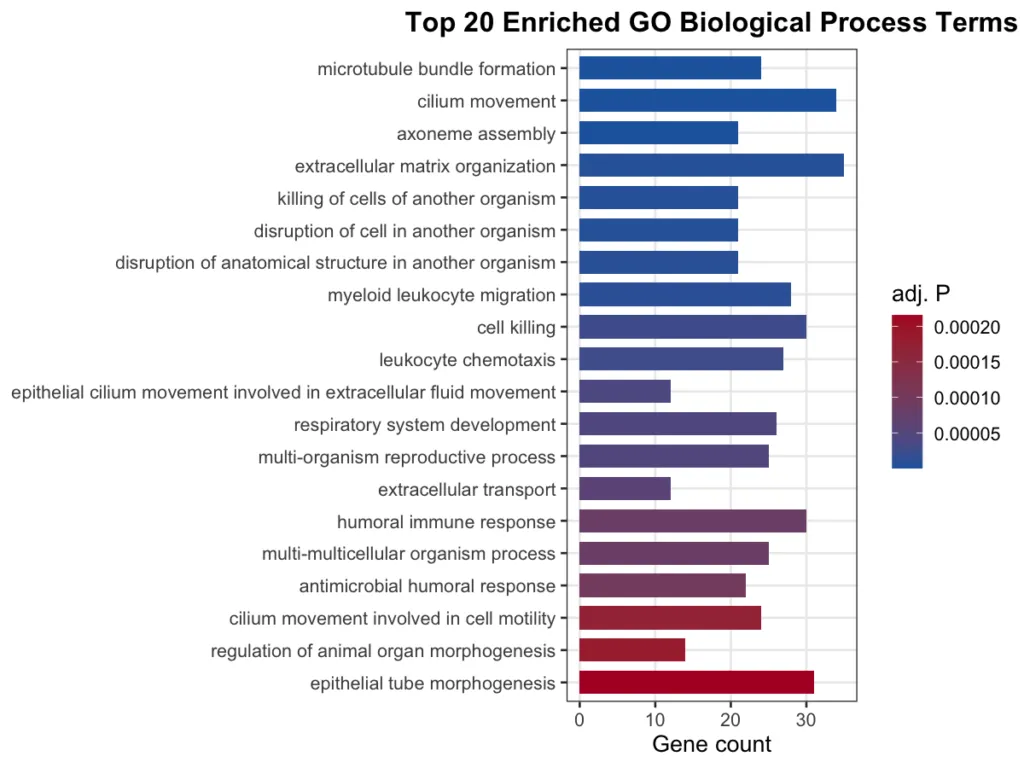
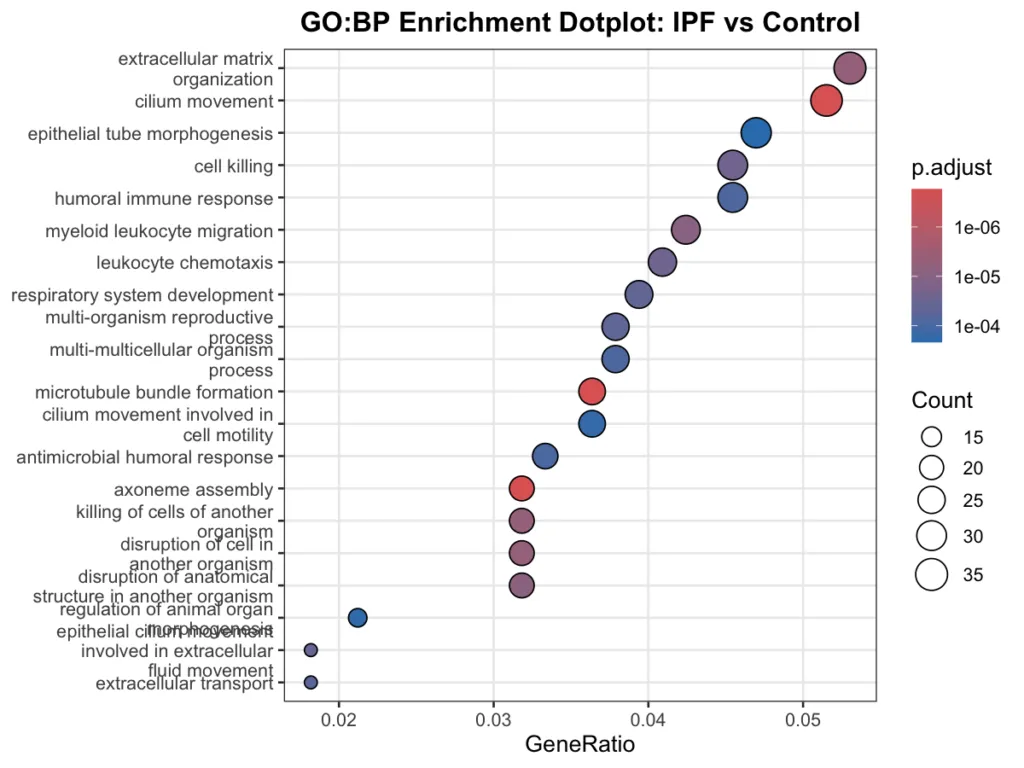
免疫応答・炎症・ECM 組織化・繊毛運動など、幅広いプロセスが有意に濃縮されていました。
Reactome
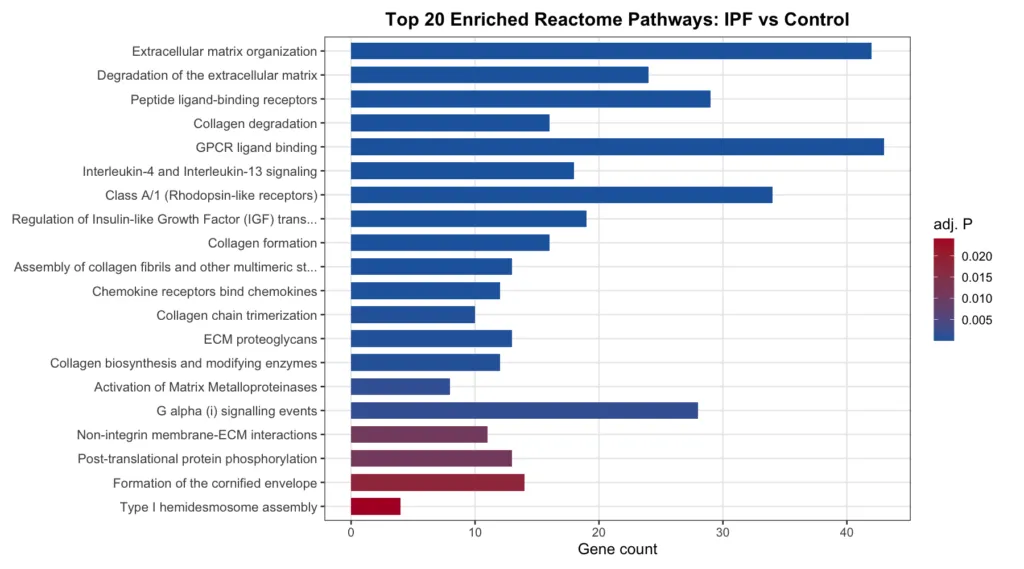
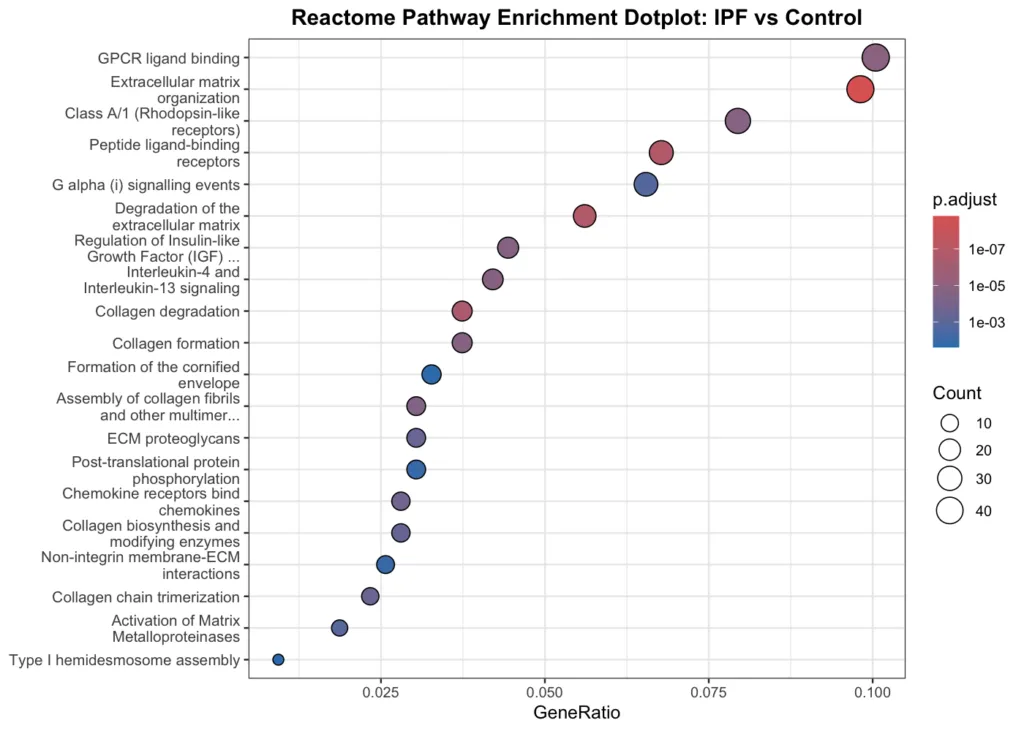
Reactome では ECM・コラーゲン代謝に関するパスウェイが上位を占めました。「Extracellular matrix organization」「Collagen biosynthesis and modifying enzymes」「Activation of Matrix Metalloproteinases」など、IPF の線維化メカニズムに直結する経路が明確に浮かび上がっています。
Step 3:CBNplot でパスウェイ間のネットワークを描く(bnpathplot)
ここからが CBNplot の本領です。
bnpathplot() は、220サンプルのパスウェイ別遺伝子発現スコアを入力として、ベイジアンネットワークを学習します。各パスウェイが「どのパスウェイの状態を説明するか」を統計的に推定し、矢印で描きます。
-
矢印の向き = 因果の方向(→ = こちらがあちらを「引き起こす」)
-
矢印の太さ = Bayesian edge strength(依存の確信度、0.5〜1.0)
GO:BP パスウェイネットワーク
全変動遺伝子
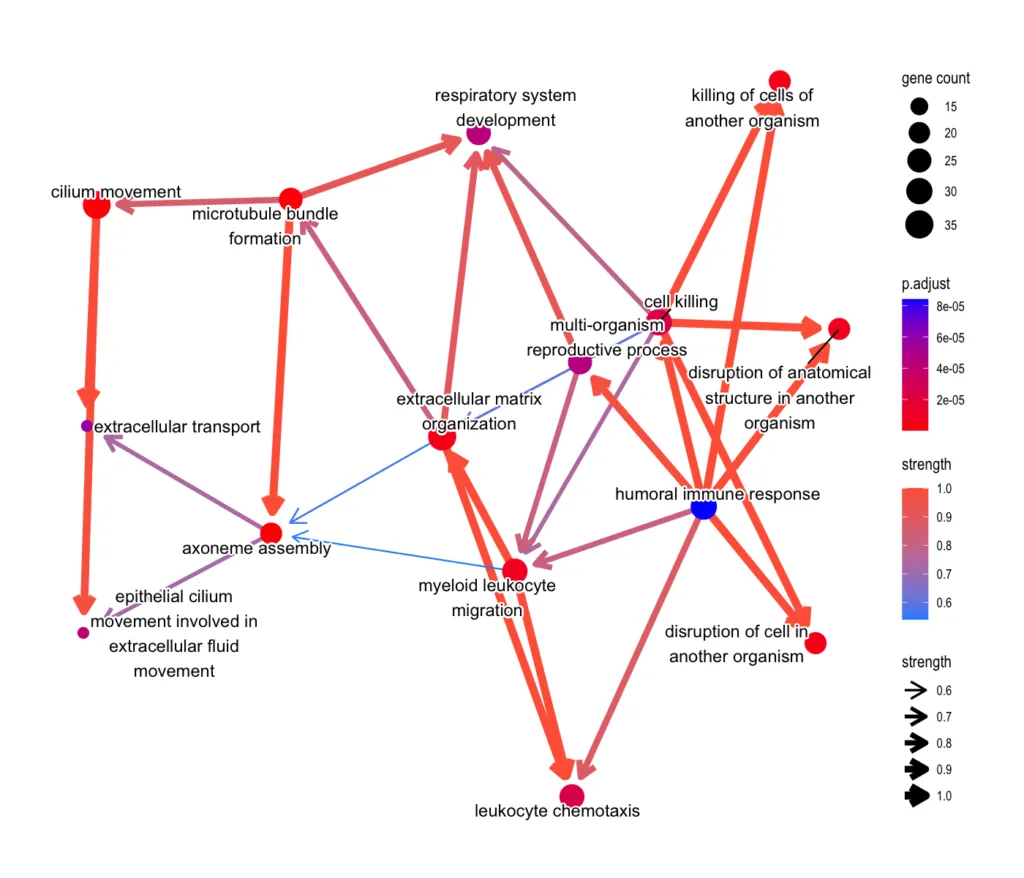
上昇遺伝子
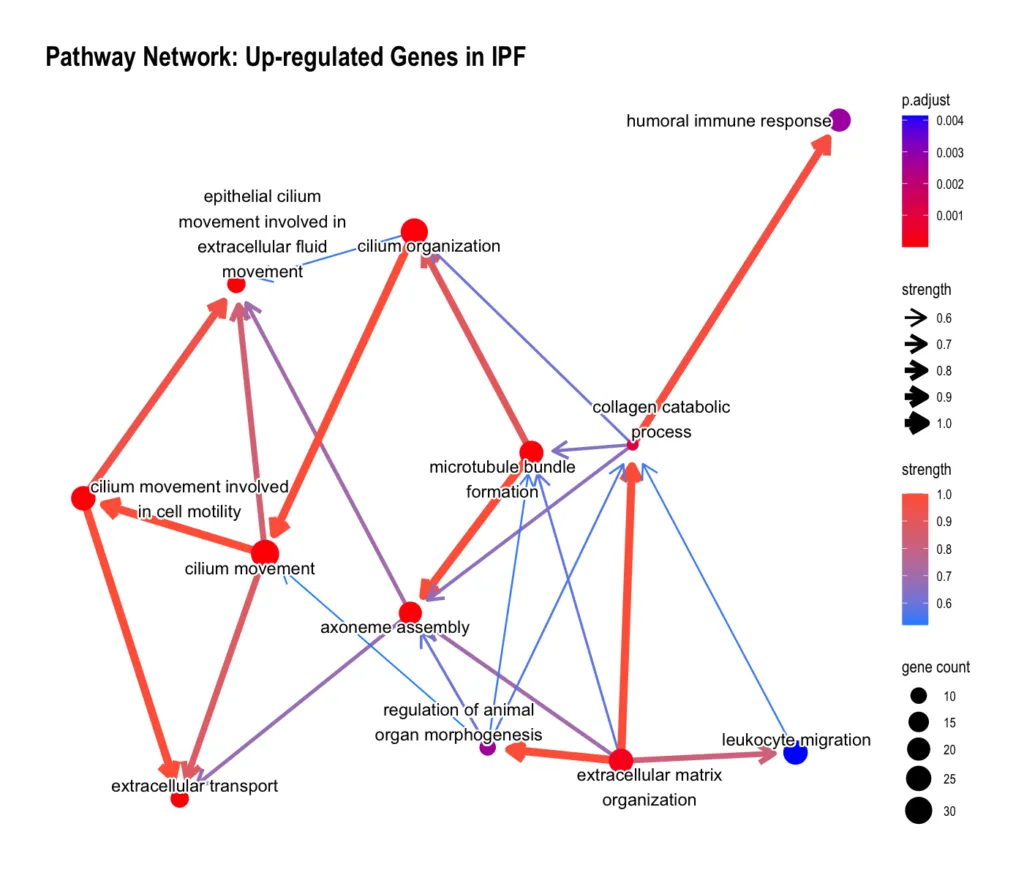
上昇遺伝子(IPFで亢進)では、免疫・炎症・ECM 関連パスウェイが密に相互接続されています。
低下遺伝子
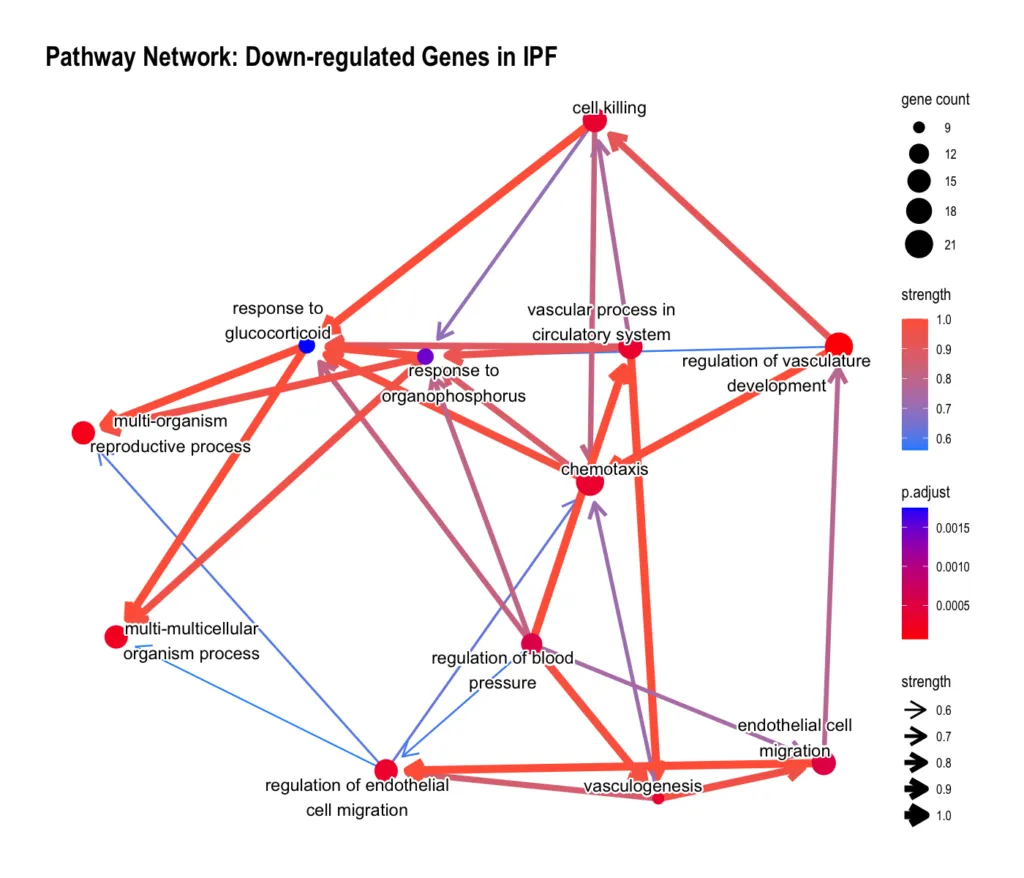
低下遺伝子(IPFで抑制)では、繊毛運動・軸索形成に関するパスウェイがまとまって変動していました。IPF では気道上皮の繊毛機能が障害されることが知られており、この結果はその知見と対応しています。
Reactome パスウェイネットワーク
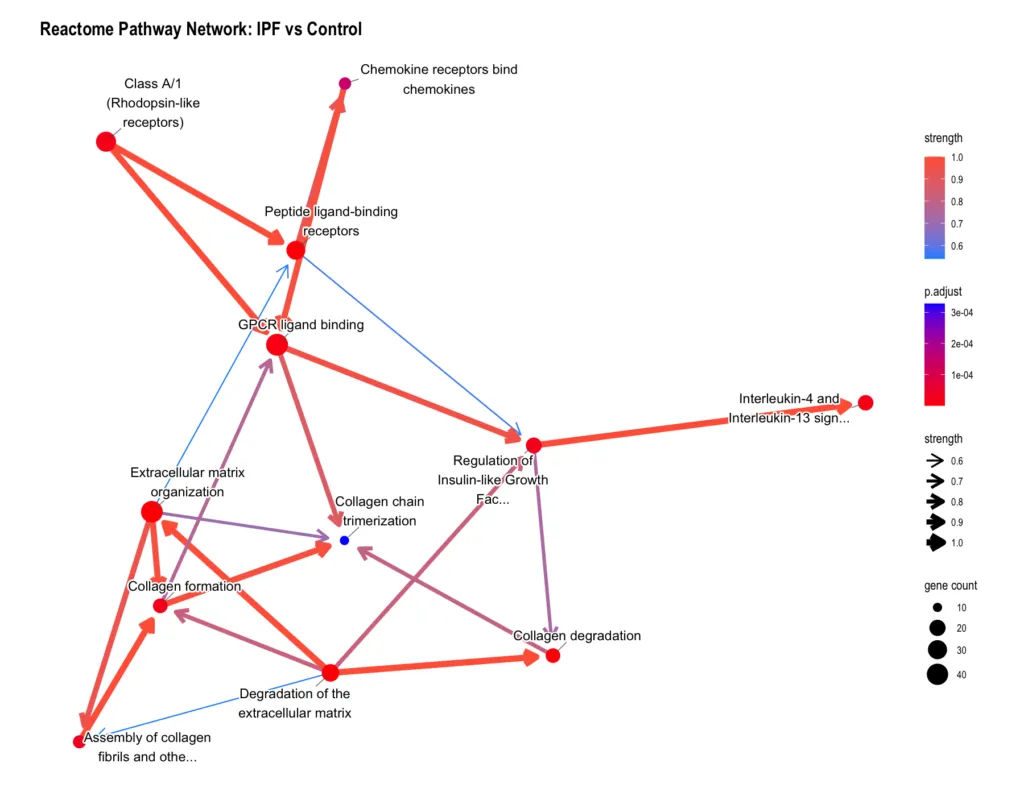
Reactome のネットワークでは、「Degradation of the extracellular matrix」が多くの矢印の起点となっており、ECM 分解がコラーゲン代謝の複数の経路を駆動していることが見えます。
Step 4:パスウェイ内の遺伝子ネットワーク(bngeneplot)
Step 3 のパスウェイネットワークから、**「ECM organization が多くの矢印を受け取るハブである」「GPCR ligand binding(ケモカインシグナル)が下流の終端に位置する」**という構造が見えてきました。
では、そのハブや終端パスウェイの中で、どの遺伝子が実際に動いているのか。bngeneplot() は、特定のパスウェイの中で遺伝子同士がどう影響し合っているかを可視化します。「パスウェイ」という面の解析から、「遺伝子」という点の解析へと掘り下げる機能です。
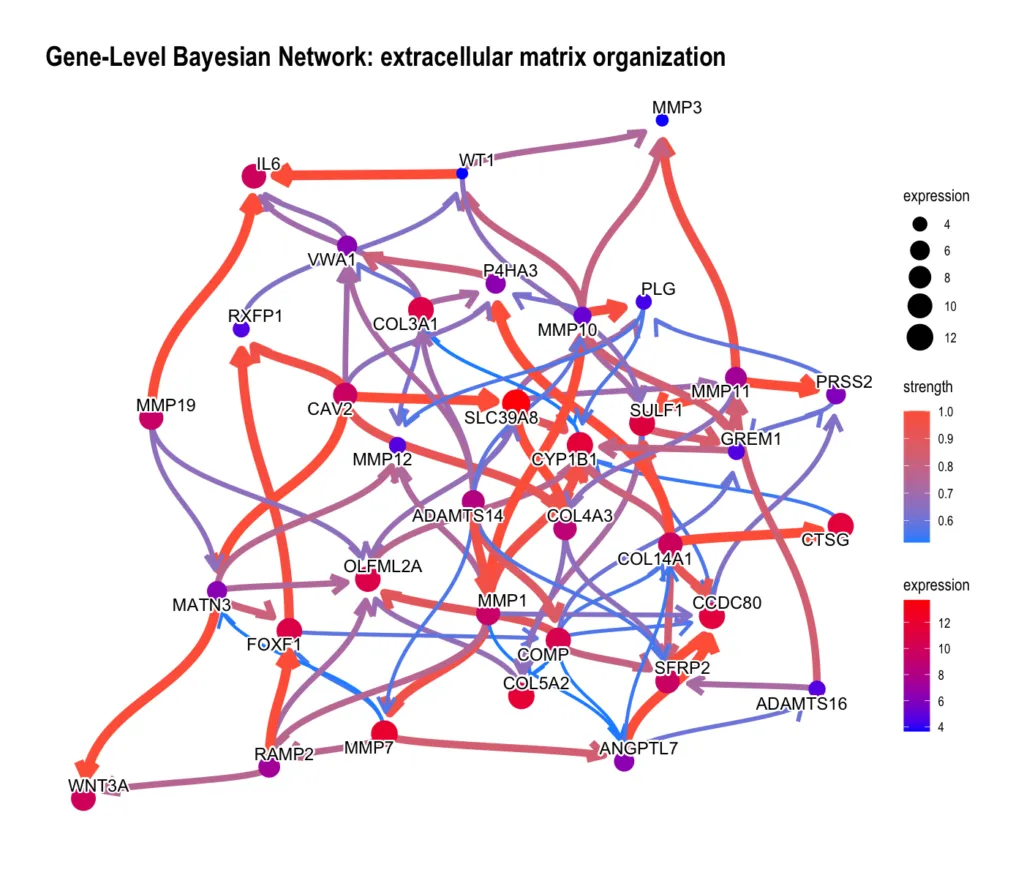
GO:BP — Extracellular matrix organization(ハブパスウェイの内部)
GO:BP ネットワークでハブとして浮かび上がった Extracellular matrix organization の内部を見ます。
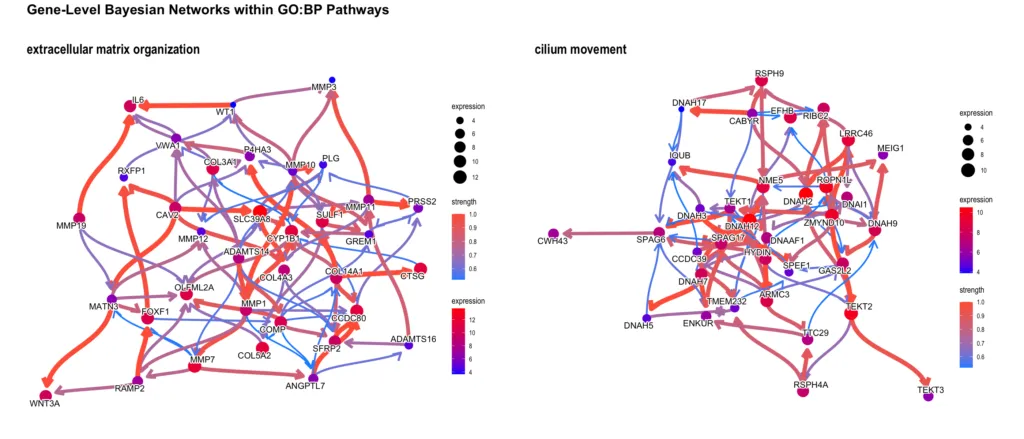
GO:BP — 複数パスウェイを横断した遺伝子ネットワーク
さらに、ハブ周辺の複数パスウェイを同時に指定することで、パスウェイをまたいで遺伝子がどうつながっているかも追えます。
Reactome — GPCR ligand binding(ネットワーク下流の終端パスウェイ)
Reactome ネットワークでは「GPCR ligand binding」がケモカイン駆動炎症の受け皿として下流に位置していました。その内部を見ると——
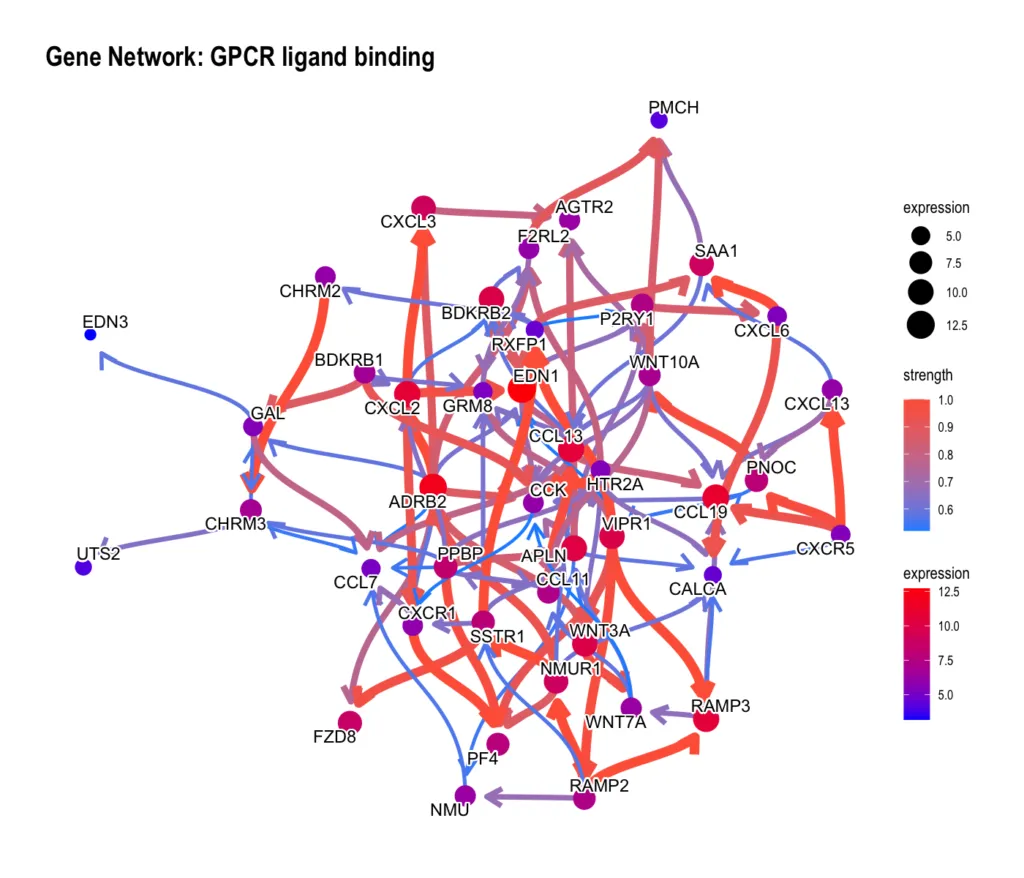
CXCL13・CCL7 などのケモカインが下流に位置しており、ECM 分解から炎症シグナルへの橋渡しとなっている遺伝子群が確認できます。Step 1 のボルカノプロットで上位に見えた遺伝子たちが、ここでも下流の結果として登場している点は注目に値します。
前編のまとめ
| ステップ | やったこと | わかったこと |
|---|---|---|
| DEG 同定 | limma | MMP1・SPP1・COL17A1 など線維化・炎症遺伝子が上昇 |
| 濃縮解析 | GO:BP + Reactome | ECM・コラーゲン代謝・免疫応答パスウェイが有意 |
| bnpathplot | CBNplot | パスウェイ間の因果方向と依存強度が可視化された |
| bngeneplot | CBNplot | パスウェイ内の遺伝子間ネットワークが明らかに |
後編では、このネットワークから**「何が起きてどうなったか」という因果のストーリーを客観的に引き出す**方法を解説します。ネットワーク指標による役割分類、因果フロー図、OpenTargets を使ったハブ遺伝子の疾患関連性検証まで踏み込みます。
関連記事ベイジアンネットワーク(CBNplot)で読み解く特発性肺線維症(IPF)— 後編:ネットワークから因果のストーリーを引き出す →